צוות חוקרים הצליח לראשונה לדמות במחשב את מחזור החיים המלא של תא חי – משכפול DNA ועד חלוקת התא. המודל המפורט מאפשר לעקוב אחרי התנהגותן של אלפי מולקולות בתוך התא בזמן אמת ולבחון בו-זמנית תהליכים ביולוגיים רבים
צוות חוקרים הצליח לראשונה לדמות במחשב את מחזור החיים המלא של תא חי – משכפול DNA ועד חלוקת התא. המודל המפורט מאפשר לעקוב אחרי התנהגותן של אלפי מולקולות בתוך התא בזמן אמת ולבחון בו-זמנית תהליכים ביולוגיים רבים.
חוקרים מאוניברסיטת אילינוי באורבנה-שמפיין הצליחו לדמות במחשב את מחזור החיים של תא חיידקי בסיסי – החל משכפול ה-DNA דרך תרגום חלבונים ומטבוליזם, ועד לחלוקת התא. העבודה פותחת חלון חדש להבנת התהליכים הבסיסיים של החיים ברזולוציה חסרת תקדים.
המחקר, בהובלת פרופ' Zan Luthey-Schulten מהמחלקה לכימיה באוניברסיטה, פורסם בכתב העת Cell.
כדי להגיע לכך נדרשו שנים של עבודה, משאבי מיחשוב עצומים, מאגרי נתונים ניסיוניים גדולים ושילוב של שיטות ניסוי וחישוב מתקדמות. החוקרים היו צריכים להביא בחשבון כל גן, חלבון, מולקולת RNA וכל תגובה כימית שמתרחשת בתא, כדי לשחזר את התזמון המדויק של האירועים התאיים. למשל, המודל היה צריך לשקף בדיוק את התהליך שבו התא מכפיל את גודלו לפני החלוקה.
כדי להפוך את המשימה לאפשרית יותר, החוקרים השתמשו בתא “מינימלי” חי שפותח במכוןJ. Craig Venter Institute בקליפורניה. התא שנבחר למחקר JCVI-syn3A או בקיצורSyn3A , הוא חיידק שעבר הנדסה גנטית כך שהגנום שלו כולל רק את הגנים ההכרחיים לקיום החיים – שכפולDNA , גדילה, חלוקה ורוב התפקודים הביולוגיים הבסיסיים.
לדברי לוטיי-שולטן:
“זהו מודל תלת-ממדי דינמי לחלוטין של תא חי עם תפקודים הכרחיים בלבד, שמחקה את מה שמתרחש בתא אמיתי. מיזם מקיף כזה התאפשר רק בזכות שיתוף פעולה רחב בין חוקרים באוניברסיטת אילינוי ובבית הספר לרפואה של הרווארד.”
לתא Syn3A יש פחות מ-500 גנים בלבד, וכולם נמצאים על גדיל DNA מעגלי יחיד. מעבדותיהם של החוקרים Angad Mehta מאוניברסיטת אילינוי ו-Taekjip Ha מבית החולים לילדים בבוסטון ובית הספר לרפואה של הרווארד, סיפקו נתונים ניסיוניים נוספים שאיפשרו לדייק את הסימולציה ולאמת היבטים שונים של פעילות התא.
לדברי לוטיי-שולטן, נתונים אלה איפשרו להבין טוב יותר את היקף שכפול ה-DNA ואת העובדה שחלוקת התא של Syn3A היא סימטרית.
את הסימולציות עצמן ביצעוZane Thornburg , עמית פוסט-דוקטורט במכון בקמן למדע וטכנולוגיה מתקדמים, ו-Andrew Maytin , סטודנט לתואר שני במעבדתה של לוטיי-שולטן.
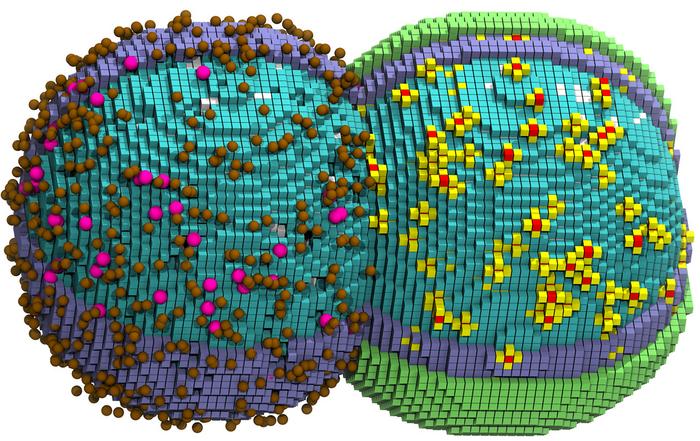
כמו חיידקים אחרים, לתא Syn3A אין גרעין. כל המולקולות שמרכיבות אותו נמצאות בציטופלזמה, בממברנה החיצונית או מגיעות אליו מבחוץ באמצעות מנגנוני הובלה. התא כה צפוף במולקולות עד שכאשר החוקרים יצרו הדמיות ברזולוציה גבוהה של הסימולציה, הם נאלצו להסתיר חלק מן הרכיבים כדי לאפשר לראות מבנים אחרים. למשל, כאשר “העלימו” את החלבונים מההדמיה, ניתן היה לראות כיצד הכרומוזום משתרג בתוך חלל התא הצפוף.
החוקרים גילו שחלק מן התהליכים בתא דורשים הרבה יותר כוח חישובי מאחרים. למשל, שכפול הכרומוזום האט משמעותית את הסימולציה והכפיל כמעט את זמן החישוב. הפתרון היה להקצות מעבד גרפי (GPU) ייעודי לשכפול ה-DNA , בעוד שמעבד גרפי נוסף טיפל בכל שאר התהליכים התאיים. כך הצליח הצוות לדמות מחזור תא מלא של105 דקות בתוך שישה ימי חישוב בלבד.
לדברי תורנבורג, אחד האתגרים הגדולים היה לדמות תהליכים שמתרחשים בו-זמנית באזורים שונים של התא.
“אי אפשר להפריז בקושי של סימולציה של דברים שנעים כל הזמן – וביצוע זאת בתלת-ממד עבור תא שלם היה הישג גדול,” אמר. “אחד האתגרים האחרונים שאנדרו ואני נאלצנו לפתור היה להבין כיצד הממברנה וה-DNA מתקשרים זה עם זה כאשר שניהם נמצאים בתנועה.”
על אף שהמודל אינו מדמה כל אטום בנפרד אלא משתמש בערכים ממוצעים לדינמיקה של מולקולות, הוא הצליח לשחזר באופן מדויק למדי את התזמון של תהליכים תאיים. בסימולציות חוזרות של תאים בעלי תנאי התחלה מעט שונים, מחזור התא המדומה התרחש בממוצע בהפרש של כשתי דקות בלבד מהמחזור האמיתי. לאורך כל הדרך נבדקו הסימולציות מול נתונים ניסיוניים אמיתיים, שאיפשרו לשפר בהדרגה את המודל.
לוטיי-שולטן אומרת שהיכולת לדמות באופן מדויק את התנאים המשתנים בתוך תא חי פותחת אפשרויות מחקר חדשות.
“יש לנו מודל של תא שלם שמנבא בו-זמנית תכונות תאיות רבות,” אמרה. “אם רוצים לדעת מה קורה למשל במטבוליזם של נוקלאוטידים, אפשר גם לראות מה מתרחש בשכפול ה-DNA או ביצירת ריבוזומים. כלומר, הסימולציה יכולה לספק תוצאות של מאות ניסויים בו-זמנית.”
בין מחברי המחקר גם בוגרי אוניברסיטת אילינויBenjamin Gilbert ו-John Glass, שמוביל את קבוצת הביולוגיה הסינתטית במכון J. Craig Venter.
המחקר בוצע במסגרת מרכז המדע והטכנולוגיה לביולוגיה תאית כמותית של הקרן הלאומית למדע האמריקנית(NSF) . החישובים נערכו באמצעות מערכת המחשוב המתקדמת:Delta המופעלת בשיתוף אוניברסיטת אילינוי והמרכז הלאומי ליישומי מחשוב-על.
המאמר:
“Bringing the genetically minimal cell to life on a computer in 4D”
כתב העת: Cell
DOI: 10.1016/j.cell.2026.02.009
עוד בנושא באתר הידען:

תגובה אחת
זה הישג hpv, אבל נראה לי שבעתיד הלא רחוק הוא יתגמד לעומת מה ש AI יעשה בעניין עם AlphaCell או משהו דומה.
אני מרגיש קצת כאילו קראתי שיש גירסה חדשה של Deep Blue עם דרוג ELO= 3500.